1. 样品:两组土壤样品同样条件培养。其中,第一组土壤(三个重复)保持75%的含水量于一周(第1天 10°C,第3天 15°C,第5天 25°C,第7天 30°C)后收集储存,第二组土壤(三个重复)一周后继续置于30°C且不再添加无菌水,经过14天完全干燥后收集储存,用于模拟炎热天气下土壤的自然干燥。
2. 实验细节:
▶ DNA用于构建二代宏基因组建库,RNA用于二代宏转录组建库
▶ 每个重复取5g样本构建宏基因组Hi-C文库(样品与25ml水混合窝旋, 1000 x g离心10min,取上清液,添加1%甲醛,室温20min,1%甘氨酸终止交联; Sau3AI和MlucI酶处理;补平标记生物素;连接;解交联;磁珠富集嵌合片段;二代建库测序)。
3. 数据分析
▶ 宏基因组数据QC:
• QC去接头、过滤低质量reads、标准化:fastp
• contig组装:MEGAHIT (v1.2.9) 和 meta-large
• 筛选病毒contig:VirSorter (v2)、VIBRANT((v1.2.1)、DeepVirfinder (v 2020.11.21)、CheckV (v0.7.0)
▶ Hi-C数据QC
• Hi-C clean reads与宏基因组contigs进行比对:BWA-MEM (v0.7.17)
• 去PCR: SAMBLASTER (v0.1.24)
• 过滤:samtools (v1.9)
▶ 宏基因组分箱和聚类
• 宏基因组组装和Hi-C互作数据通过ProxiMeta聚类得到宏基因组组装基因组(MAG)
• CheckM (v1.2.0) 评估分箱基因组或MAG的质量
• dRep对MAGs进行去冗余。
• CheckM对去冗余后的MAGs进行分类注释。
• GTDB-Tk对CheckM的分类结果进行验证。
• 分析标准化后的reads的测序深度来估计MAGs的丰度。
▶ DNA病毒序列聚类和注释
• A greedy centroid algorithm聚类得到vOTU:95% ANI and 85% AF
• 注释:Demovir工具,TrEMBL数据库中病毒参考序列
▶ 宏基因组和宏转录组中的DNA病毒丰度
• 宏基因组:BBMap (v 38.34)
• 宏转录组: BamM(v1.7.3)比对过滤, samtools(v1.9)
▶ 噬菌体-宿主关联:
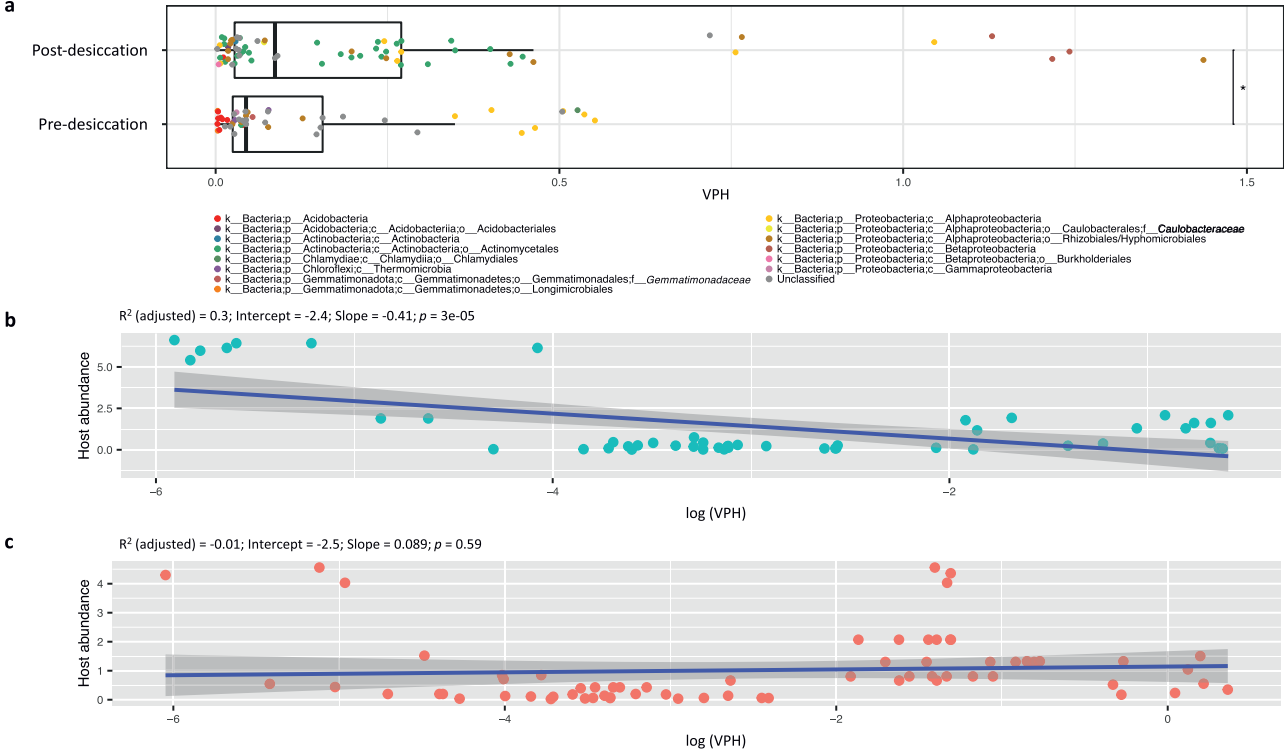
• 通过Hi-C reads筛选噬菌体-宿主互作,该数据可用于计算每个宿主的平均病毒拷贝数(VPH)
 027-87224696
|
027-87224696
| marketing@frasergen.com
|
marketing@frasergen.com
|



 微信公众号
微信公众号

